Durante anos, os investigadores acreditaram que o ADN dentro de um óvulo recentemente fertilizado começava como uma “lousa em branco” estrutural – um feixe solto e desorganizado que só ganharia ordem quando o embrião começasse a usar os seus próprios genes. Nessa visão tradicional, o genoma estava em grande parte desorganizado até “acordar” e iniciar o seu programa genético.
Nova pesquisa foi publicada Genética da natureza Acho que o desafio durou tanto tempo. A professora Juanma Vaquerizas e seus colegas relatam que o genoma já mostra um nível inesperado de organização nesta fase inicial. A equipe desenvolveu uma nova tecnologia chamada Pico-C que permite aos cientistas examinar a estrutura 3D do genoma com detalhes notáveis. Com este método, eles descobriram que mesmo antes de o genoma ser totalmente ativado – um marco conhecido como ativação do genoma zigótico – uma elaborada estrutura 3D de DNA já está tomando forma.
Este padrão inicial de dobramento não é apenas uma curiosidade estrutural. A forma como o DNA está organizado no espaço determina quais genes podem ser ativados durante o desenvolvimento. Essa regulação é essencial para o funcionamento adequado das células e ajuda a prevenir anomalias de desenvolvimento e doenças.
“Antes do despertar do genoma, pensávamos nele como um período de caos”, explica Nora Maziak, principal autora do estudo. “Mas, aproximando-nos mais do que nunca, podemos ver que este é, na verdade, um local de construção altamente ordenado. A estrutura do genoma está a ser construída de uma forma precisa e modular, muito antes de o botão ‘ligar’ ser completamente ligado.”
Tecnologia Pico-C mapeia dobramento de DNA em moscas-das-frutas
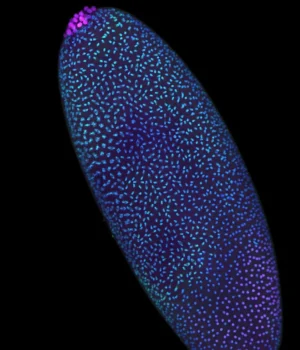
A descoberta foi feita a partir da mosca da fruta (Drosophila), organismo modelo amplamente utilizado em pesquisas genéticas. Durante as primeiras horas após a fertilização, o embrião de uma mosca da fruta divide rapidamente o seu núcleo, produzindo milhares de células num curto período de tempo. Este rápido ritmo de desenvolvimento torna-o um sistema ideal para estudar como os genomas são organizados e regulados.
Usando seu método pico-C altamente sensível, os pesquisadores mapearam a estrutura 3D do genoma da mosca da fruta nesta fase inicial. Eles descobriram que o DNA se enrola e se dobra em um padrão modular, permitindo que diferentes sinais regulatórios afetem regiões específicas do genoma. Esta arquitetura complexa garante que a informação genética seja preparada e posicionada para ativação quando necessário.
Além de fornecer visualizações detalhadas da estrutura do DNA, o pico-C requer apenas amostras muito pequenas – cerca de dez vezes menos material do que as técnicas padrão. Essa capacidade torna possível investigar como o dobramento do DNA molda a regulação genética e como esses distúrbios arquitetônicos podem contribuir para doenças com maior precisão.
Quando a arquitetura do genoma se decompõe nas células humanas
Embora o “modelo” estrutural tenha sido identificado pela primeira vez em moscas-das-frutas, a sua relevância estende-se à biologia humana. Em um estudo complementar publicado Biologia Celular da Natureza Os investigadores, liderados pelo professor Ulrik Kutte e colegas da ETH Zurich, na Suíça, aplicaram a mesma técnica de mapeamento de alta resolução a células humanas.
Eles examinaram o que acontece quando as “âncoras” moleculares que estabilizam a estrutura 3D do genoma são removidas. Os resultados foram interessantes. Quando esta estrutura estrutural se desintegra, as células humanas interpretam a degradação como se estivessem sob ataque viral. Esta interpretação errada ativa o sistema imunológico inato da célula, criando um alarme falso que pode levar à inflamação e à doença.
“Esses dois estudos contam uma história completa”, disse Juanma. “O primeiro mostra-nos como a estrutura 3D do genoma é cuidadosamente elaborada no início da vida. O segundo mostra-nos que se a estrutura se decompor, haverá consequências catastróficas para a saúde humana.”
Esta pesquisa foi financiada pelo Conselho de Pesquisa Médica e pela Academia de Ciências Médicas (AMS) por meio de um prêmio de Professor da AMS.